Cartografía genética
La cartografía genética es una disciplina de la genética que, mediante varias técnicas, busca asignar a los distintos genes de un genoma su lugar físico en aquel. Existen dos variantes fundamentales de mapas: los genéticos, definidos mediante unidades de frecuencia de recombinación, y los físicos, en los que las distancias entre loci se expresan en unidades de distancia en nucleótidos.[1]
Descubrimiento del ligamiento
[editar]Tras los estudios de genética clásica sobre la transmisión de caracteres independientes por parte de Mendel que condujeron en el siglo XIX a la formulación de sus leyes,[2] otros investigadores, William Bateson y R. C. Punnet, encontraron en 1911 una desviación a este tipo de herencia al estudiar la segregación de cruzamientos entre dos líneas de flores que diferían en dos caracteres dados.[3] Aunque la base física de esta peculiaridad se desconocía en la época, dicha anomalía se debe a que aquellos caracteres se encontraban acoplados físicamente en el cromosoma: esto es, se encontraban ligados, a diferencia de los estudiados por Mendel, que se encontraban en cromosomas distintos. De esta manera, la tasa de recombinantes producidos tras el cruce de los parentales era menor a la esperada, debido a que, por cercanía física en la hebra de ADN, la probabilidad de que se produjese un evento de recombinación, un quiasma, era pequeña, e inversamente proporcional a la distancia entre los dos loci codificantes de esos caracteres. En cambio, en el modelo inicial de Mendel, la probabilidad de recombinación, de 0,5, expresaba la transferencia aleatoria de uno u otro alelo de cada carácter debido a la transferencia al azar hacia el gameto de uno u otro cromosoma homólogo durante la meiosis.[1]
Análisis basados en la recombinación
[editar]Se define recombinación meiótica como cualquier proceso meiótico que da lugar a un genotipo haploide distinto de los dos genotipos haploides cuya fusión dieron lugar a la célula meiótica diploide. Esto es, la recombinación meiótica da lugar a recombinantes. Dicha recombinación puede proceder tanto de una segregación independiente como de una la existencia de entrecruzamientos.[1]
En el caso de la segregación independiente, se observa que, al cruzar dos líneas puras, la progenie resultante es heterocigótica en su totalidad. De efectuar un cruzamiento de prueba, es decir, un cruce de la primera generación filial, la F1 heterocigótica en este caso, con uno de los parentales, que es una línea pura, se obtiene una distribución genotípica en la cual el porcentaje de recombinantes es de la mitad de la progenie: existe un 25 % de cada tipo recombinante.
En cuanto a los recombinantes obtenidos mediante entrecruzamiento, estos se producen mediante hechos de recombinación entre cromátidas no hermanas en un lugar entre dos loci dados. Tras el entrecruzamiento, la mitad de los productos de esa meiosis son recombinantes para esos dos loci.
Técnicas
[editar]FISH
[editar]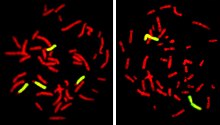
La hibridación fluorescente in situ es una técnica que se basa en la unión selectiva de un polinucleótido de cadena sencilla y de secuencia dada (denominado sonda) a una o más zonas del genoma que posean secuencias complementarias, en una preparación de células o tejidos. Dicha unión se observa mediante un microscopio de fluorescencia o un microscopio confocal, puesto que la sonda está marcada mediante un fluorocromo.[4] Dicha técnica se emplea sobre muestras histológicas en los que los ácidos nucleicos han sido fijados: por ejemplo, puede emplearse sobre células en estado metafásico (debido a un tratamiento previo con colchicina o colcemida) lo cual puede permitir asignar un marcador a un cromosoma concreto. No obstante, también es posible emplear la técnica sobre núcleos interfásicos.[5]
RFLP
[editar]Un RFLP (siglas en inglés de restriction fragment length polimorphism, es decir, «polimorfismo en la longitud del fragmento de restricción») representa un polimorfismo asociado generalmente a una mutación puntual en un punto determinado de un genoma. Se detecta mediante la digestión mediante enzimas de restricción de ADN genómico o bien de un amplicón producido mediante PCR previamente (en este último caso, se habla de CAPS o Cleaved Amplified Polymorphic Sequence, o polimorfismo de fragmento amplificado y digerido).[6]

Una forma de detectar dicho polimorfismo es mediante Southern blot. Para ello se digiere el ADN genómico de dos individuos con una enzima y luego se hibrida la mezcla de fragmentos resultante con una sonda marcada que hibrida en la zona de la diana que muestra polimorfismo. De este modo, puede detectarse luego el tamaño de los fragmentos generados. En el gráfico se observa: un individuo A que es homocigótico para la ausencia de diana, luego muestra en el southern una única banda de 5 KB (el tamaño acotado por dos dianas de restricción para la enzima empleada); y un heterocigoto, que muestra la misma banda de 5 KB (procedente de su cromosoma homólogo "sin diana") más dos bandas (de 3 y 2 KB, pues la sonda complementa con una secuencia en ambos fragmentos, pues estos colindaban en origen con la diana de restricción).[7]
Cartografía mediante deleciones
[editar]
Las deleciones son mutaciones que ocasionan la pérdida de fragmentos de ADN. Empleando cruzamientos de mutantes, las deleciones pueden permitir la topología de una determinada secuencia. En la imagen de ejemplo se observa el genotipo de dos mutantes para un gen con cinco segmentos: el mutante de arriba sólo contiene los segmentos 1, 2 y 3; y el de abajo, el 3, 4 y 5. Un mutante nuevo que produzca recombinantes con fenotipo silvestre al cruzarse con el de abajo estará mutado en un sitio en el área A. Uno que los produzca al cruzarse con el de arriba pero no con el de abajo estará mutado en la región C.[1]
Este método permitió a Seymour Benzer definir la topología del gen, es decir, la forma en que están interconectadas sus partes.[8]
Referencias
[editar]- ↑ a b c d Griffiths, J .F. A. et al. (2002). Genética. McGraw-Hill Interamericana. ISBN 84-486-0368-0.
- ↑ Artículo original de Mendel, en inglés: Gregor Mendel (1865). «Experiments in Plant Hybridization».
- ↑ W. Bateson and R. C. Punnett (1911). «On the Inter-Relations of Genetic Factors». Proceedings of the Royal Society of London. Series B, Containing Papers of a Biological Character 84 (568). pp 3-8.
- ↑ Trask BJ. Fluorescence in situ hybridization: applications in cytogenetics and gene mapping. Archivado el 15 de febrero de 2009 en Wayback Machine. Trends in Genetics Volume 7, Issue 5, May 1991, Pages 149-154
- ↑ Trask BJ. DNA sequence localization in metaphase and interphase cells by fluorescence in situ hybridization. Methods Cell Biol. 1991;35:3-35.
- ↑ Paul Jarvis, Clare Lister, Veronique Szabo and Caroline Dean. Integration of CAPS markers into the RFLP map generated using recombinant inbred lines of Arabidopsis thaliana Plant Molecular Biology, 1994 - Springer. DOI 10.1007/BF00023565
- ↑ Watson, J, D.; Baker, T. A.; Bell, S. P.; Gann, A.; Levine, M. et Losick, R (2004). Molecular Biology of the Gene (Fifth edition edición). San Francisco: Benjamin Cummings. ISBN 0-321-22368-3.
- ↑ S Benzer (1961). On the Topography of the Genetic Fine Structure PNAS 1961 47:403-415.